



| General Information: |
|
| Name(s) found: |
RCK1_YEAST
[Swiss-Prot]
|
| Description(s) found: |
|
| Organism: | Saccharomyces cerevisiae S288c |
| Length: | 512 amino acids |
Gene Ontology: |
|
| Cellular Component: | NONE FOUND |
| Biological Process: | NONE FOUND |
| Molecular Function: | NONE FOUND |
| Sequence: |
|
| Sequence: [PDR BLAST] [ProtParam] |
1 11 21 31 41 51
| | | | | |
1 MSVNPEFIAD GIDFYPTTPD AAYFNAADGK NKVNRINGNS ENLHHSFASG CRRSSLSVDF 60
61 NVTSSDSEKS EQSCLENNSQ EDEYFCDIFS TELKLDETSN KSTDYSSSNH QYPEQLELHN 120
121 YKLLNKIGEG AFSRVFKAVG INTDDQAPVA IKAIIKKGIS SDAILKGNDR IQGSSRKKVL 180
181 NEVAIHKLVS KNNPHCTKFI AFQESANYYY LVTELVTGGE IFDRIVQLTC FSEDLARHVI 240
241 TQVAIAIKHM HYMGIVHRDV KPENLLFEPI PFYGLDGDMQ KEDEFTLGVG GGGIGLVKLM 300
301 DFGLAKKLRN NTAKTPCGTI EYVASEVFTS KRYSMKVDMW SIGCVLFTLL CGYPPFYEKN 360
361 EKTLLKKISR GDYEFLAPWW DNISSGAKNA VTHLLEVDPN KRYDIDDFLN DPWLNSYDCL 420
421 KDSNSNSYAS VQSILNDSFD ERAETLHCAL SCQSEKQDDT EFSRSESSEY IFMTEEDRNL 480
481 RGSWIGEPKE CFTLDLATSS IYRRRKNKIF FW |
NOT SHOWING SINGLE HITS. [ Show Single Hits ]
New Feature: Upload Your Own Microscopy Data
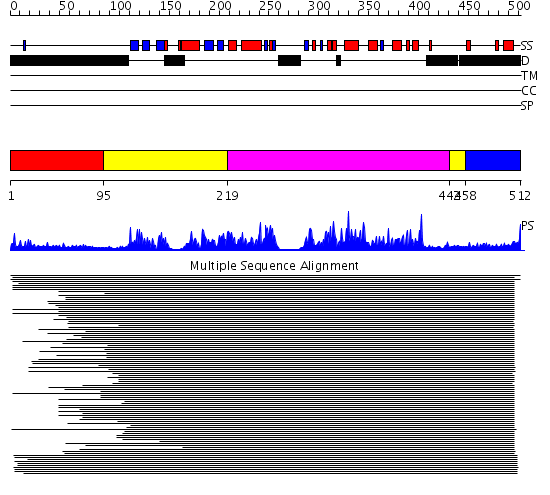
Domains predicted:
| # | Region(s) | Method | Confidence | Match Description | |
| 1 | View Details | [1..94] | N/A | No confident structure predictions are available. | |
| 2 | View Details | [95..218] [442..457] |
623.228787 | Calmodulin-dependent protein kinase | |
| 3 | View Details | [219..441] | 623.228787 | Calmodulin-dependent protein kinase | |
| 4 | View Details | [458..512] | 2.154902 | No description for 1lj6A_ was found. |
Functions predicted (by domain):
| # | Gene Ontology predictions | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 1 |
|
|||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 2 | No functions predicted. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 3 | No functions predicted. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 4 | No functions predicted. |
| Protein predicted to be: | GLOBULAR (No transmembrane regions or signal peptide) |
| Confidence of classification: | 0.84 |
Source: Reynolds et al. (2008)